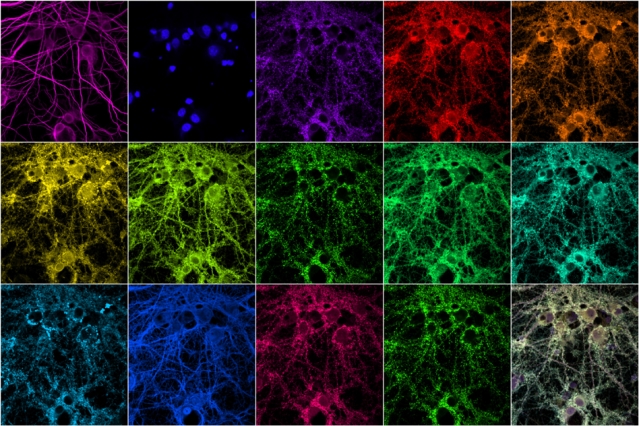
Immagine, Credit Syuan-Ming e LI LI
Il nostro cervello contiene milioni di sinapsi, le connessioni che trasmettono messaggi da neurone a neurone. All’interno di queste sinapsi ci sono centinaia di proteine diverse e la disfunzione di queste proteine può portare a condizioni come la schizofrenia e l’autismo.
“L’imaging multiplex è importante perché c’è così tanta variabilità tra sinapsi e cellule, anche all’interno dello stesso cervello”, afferma Mark Bathe, Professore associato di ingegneria biologica del MIT. “Devi davvero guardare simultaneamente le proteine nel campione per capire che aspetto hanno le sottopopolazioni di diverse sinapsi, scoprire nuovi tipi di sinapsi e capire come le variazioni genetiche incidono su di esse“.
I ricercatori hanno in programma di utilizzare questa tecnica per studiare cosa succede alle sinapsi quando viene bloccata l’espressione di geni associati a malattie specifiche, nella speranza di sviluppare nuovi trattamenti che potrebbero invertire tali effetti.
Bathe e Jeff Cottrell, Direttore della ricerca traslazionale presso lo Stanley Center for Psychiatric Research presso il Broad Institute, sono gli autori senior dello studio che appare oggi in Nature Communications. Gli autori principali dell’articolo sono gli ex postdoc Syuan-Ming Guo e Remi Veneziano, l’ex studente laureato Simon Gordonov e l’ex ricercatore Li Li.
Imaging con DNA
Le proteine sinaptiche hanno una varietà di funzioni. Molte di esse aiutano a formare scaffold sinaptici, che sono coinvolti nella secrezione dei neurotrasmettitori e nell’elaborazione dei segnali in arrivo. Mentre le sinapsi contengono centinaia di queste proteine, la microscopia a fluorescenza convenzionale è limitata all’imaging al massimo di quattro proteine alla volta.
Per aumentare questo numero, il team del MIT ha sviluppato una nuova tecnica basata su un metodo esistente chiamato DNA PAINT. Usando questo metodo, originariamente ideato da Ralf Jungmann del Max Planck Institute of Biochemistry, i ricercatori identificano le proteine o altre molecole di interesse con una sonda DNA-anticorpo. Quindi, riprendono ciascuna proteina fornendo un DNA “oligo” fluorescente che si lega alle sonde DNA-anticorpo
I filamenti di DNA hanno un’affinità intrinsecamente bassa l’uno con l’altro, quindi si legano e si sciolgono periodicamente, creando una fluorescenza lampeggiante che può essere riprodotta mediante microscopia a super risoluzione. Tuttavia, l’imaging di ogni proteina richiede circa mezz’ora, il che rende questa tecnica poco pratica per l’imaging di molte proteine in un grande campione.
Bathe e i suoi colleghi hanno deciso di creare un metodo più rapido che consentisse loro di analizzare un numero enorme di campioni in un breve periodo di tempo. Per ottenere ciò, hanno alterato la sonda di imaging del DNA-dye in modo che si legasse più strettamente all’anticorpo del DNA, usando quelli che sono chiamati acidi nucleici bloccati. Ciò fornisce un segnale molto più luminoso, quindi l’imaging può essere eseguita più rapidamente, ma a una risoluzione leggermente inferiore.
“Quando eseguiamo 12 o 15 colori su un singolo pozzo di neuroni, l’intero esperimento impiega un’ora, rispetto a una notte per l’equivalente in super-risoluzione”, afferma Bathe.
I ricercatori hanno utilizzato questa tecnica per etichettare 12 diverse proteine presenti nella sinapsi, tra cui proteine per impalcature, proteine associate al citoscheletro e proteine note per contrassegnare sinapsi eccitatorie o inibitorie. Una delle proteine che hanno esaminato è Shank3, è una proteina dell’impalcatura che è stata collegata sia all’autismo che alla schizofrenia.
Vedi anche, Visualizzazione delle sinapsi di nuova formazione con una risoluzione senza precedenti.
Analizzando i livelli di proteine in migliaia di neuroni, i ricercatori sono stati in grado di determinare gruppi di proteine che tendono ad associarsi tra loro più spesso rispetto ad altre e di imparare come diverse sinapsi variano nelle proteine che contengono. Questo tipo di informazioni potrebbe essere usato per aiutare a classificare le sinapsi in sottotipi che potrebbero aiutare a rivelare le loro funzioni.
“Inibitori ed eccitatori sono i tipi di sinapsi canoniche, ma si ipotizza che ci siano numerosi sottotipi di sinapsi diversi, senza alcuna reale conoscenza su ciò che sono”, dice Bathe.
Capire la malattia
I ricercatori hanno anche dimostrato di poter misurare i cambiamenti nei livelli di proteine sinaptiche che si verificano dopo che i neuroni sono stati trattati con un composto chiamato tetrodotossina (TTX), che rafforza le connessioni sinaptiche.
“Usando l’immunofluorescenza convenzionale, in genere è possibile estrarre informazioni da tre o quattro target all’interno dello stesso campione, ma con la nostra tecnica siamo stati in grado di espandere quel numero a 12 target diversi all’interno dello stesso campione. Abbiamo utilizzato questo metodo per esaminare il rimodellamento sinaptico che si verifica in seguito al trattamento con TTX e la nostra scoperta ha confermato un precedente lavoro che ha rivelato una sovraregolazione coordinata delle proteine sinaptiche a seguito del trattamento con TTX “, afferma Eric Danielson, senior postdoc del MIT che è autore dello studio.
I ricercatori stanno ora usando questa tecnica, chiamata PRISM, per studiare come la struttura e la composizione delle sinapsi sono influenzate dall’eliminazione dei geni associati a vari disturbi. Il sequenziamento dei genomi di persone con disturbi come l’autismo e la schizofrenia ha rivelato centinaia di varianti genetiche legate alla malattia e, per la maggior parte di tali varianti, gli scienziati non hanno idea di come contribuiscano alla malattia.
“Comprendere in che modo la variazione genetica influisce sullo sviluppo dei neuroni nel cervello e sulla loro struttura e funzione sinaptica è una grande sfida per le neuroscienze e per capire come si presentano queste malattie”, afferma Bathe.
Fonte, NewsMit